 |
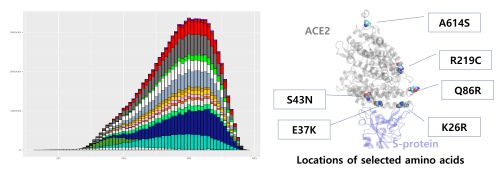
| ▲ 20만 명 규모의 바이오빅데이터 분석과 슈퍼컴퓨터 기반의 SARS-CoV-2 구조 분석 (사진=한국과학기술정보연구원 제공) |
[mdtoday=김동주 기자] 한국과학기술정보연구원(KISTI)이 KISTI 슈퍼컴퓨터 누리온을 활용해 개인 유전형 변이에 따른 hACE2 단백질 구조의 다양성을 탐색하고 이에 따른 COVID-19 바이러스 SARS-CoV-2와 결합에너지의 변화를 도출했다고 14일 밝혔다.
hACE2 단백질은 코로나 바이러스가 인간 세포에 접합하기 위한 세포막의 단백질이며, SARS-CoV-2와의 결합에너지 크기가 감염 저항성에 영향을 미칠 것으로 기대되고 있다.
이번 슈퍼컴퓨팅 기반 연구는 영국 UKBiobank에서 수집된 20만 명 규모의 유전변이 및 COVID-19 감염 검사 데이터를 분석하고, 해당 분석결과와 KISTI 슈퍼컴퓨터 누리온을 활용해 계산한 SARS-CoV-2 바이러스 결합에너지를 비교하여 수행했다.
특히 한국과학기술정보연구원 슈퍼컴퓨팅응용센터 바이오의료팀은 생물정보학 분야의 전문성을 바탕으로 영국의 대규모 유전변이 데이터를 분석하고, 슈퍼컴퓨팅 계산으로 SARS-CoV-2의 스파이크 단백질과 hACE2 단백질의 결합력 측정을 빠르고 효과적으로 수행했다.
연구책임자인 백효정, 서상재 박사는 “이번 hACE2 관련 유전변이에 따른 COVID-19 바이러스 결합 연구는 영국의 실제 COVID-19 감염 검사 데이터를 활용해 그 의미가 크다”며 “국내에서도 바이오 빅데이터가 축적되고 이를 통해 신규 감염병 대응 연구가 효율화되기를 기대한다”라고 말했다.
KISTI 정민중 슈퍼컴퓨팅응용센터장은 “팬데믹 이후 유전체 및 보건 의료 분야의 슈퍼컴퓨팅 응용연구가 활발해져 다양한 사회문제가 해결되기를 기대한다”라고 전했다.
한편 이번 연구 내용은 생물 정보학 분야의 주요 국제 저널인 ‘PLoS Computational Biology’에 온라인 게재됐다.
메디컬투데이 김동주 ([email protected])

[저작권자ⓒ 메디컬투데이. 무단전재-재배포 금지]